Incertezza dal Sante 12682/2019 – parte 2
L’articolo descrive la modalità di calcolo dell’incertezza dai proficiency test.
In altre parole con un metodo/procedura si quantifica il parametro da associare al risultato della prova.
Nel caso specifico il metodo/procedura di prova è stato impiegato per analizzare il tenore di residui dei pesticidi in uno specifico proficiency test (PT) (vedi EURL).
Calcolo incertezza dai proficiency test
Il calcolo dell’incertezza dai proficiency test è tratto dal documento Sante 12682/2019 scaricabile dal sito internet dell’EURL.
Impiegando il metodo di prova per l’analisi dei pesticidi, l’approccio deriva da una MU generica basato su una combinazione complessiva di precisione intra-laboratorio e bias calcolato dai PT.
Con questa modalità di calcolo si controlla l’incertezza complessiva a livello di metodo/procedura di prova.
Nel caso specifico il metodo di prova utilizzato dal laboratorio per l’analisi dei residui di pesticidi negli alimenti di origine vegetale è descritto nella norma UNI EN 15662:2018.
Per calcolare l’incertezza composta viene usata l’equazione 11:
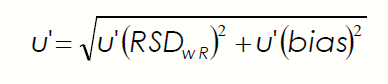
dove:
- U’: rappresenta l’incertezza composta;
- RSDwR: è il contributo di incertezza dovuto alla precisione espressa come scarto tipo;
- bias: è il contributo all’incertezza conseguente al bias ottenuto dal laboratorio partecipando ai PT
Calcolo dell’incertezza
Per valutare il contributo di precisione si suggerisce di utilizzare i dati di recupero del controllo di qualità (QC) a lungo termine.
I dati dei recuperi provenienti dalla validazione del metodo di prova possono essere utilizzati allo scopo.
La variabilità generata dalla taratura è considerata nelle prove di recupero del QC a lungo termine.
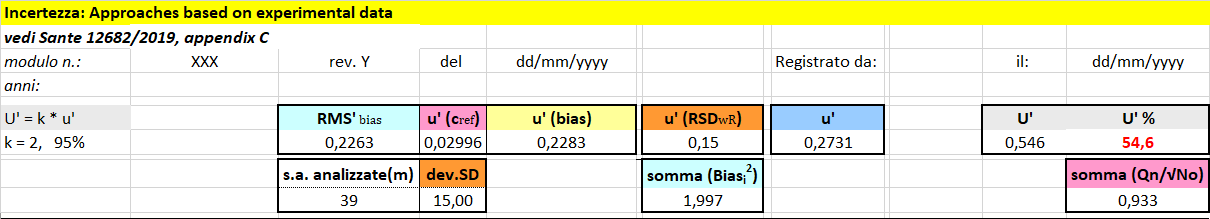
Esempio di calcolo
Riportiamo un esempio di calcolo eseguito in Excel riproducendo l’esempio del documento Sante 12682/2019.
L’esempio esaminato prevede l’impiego di un modello statistico con un minimo di 31 risultati. Per questo motivo potrebbero servire uno o più anni di risultati dei PT (vedi campi: anni e code PT).
Nel caso specifico sono stati esaminati 39 parametri (pesticides: seconda colonna), analizzati in cromatografia liquida e gassosa, ed i rispettivi recuperi (R%: quarta colonna).
Si fa riferimento a valori ottenuti in fase di validazione del metodo di prova ed anche i valori di QC di lungo periodo (range di recupero accettabile 60-140%).
Descrizione delle colonna della tabella 1
Si fa riferimento alle descrizioni riportate nella riga di colore aranciato.
Dalla partecipazione ai PT servono i seguenti dati raccolti nelle colonne di colore bianco:
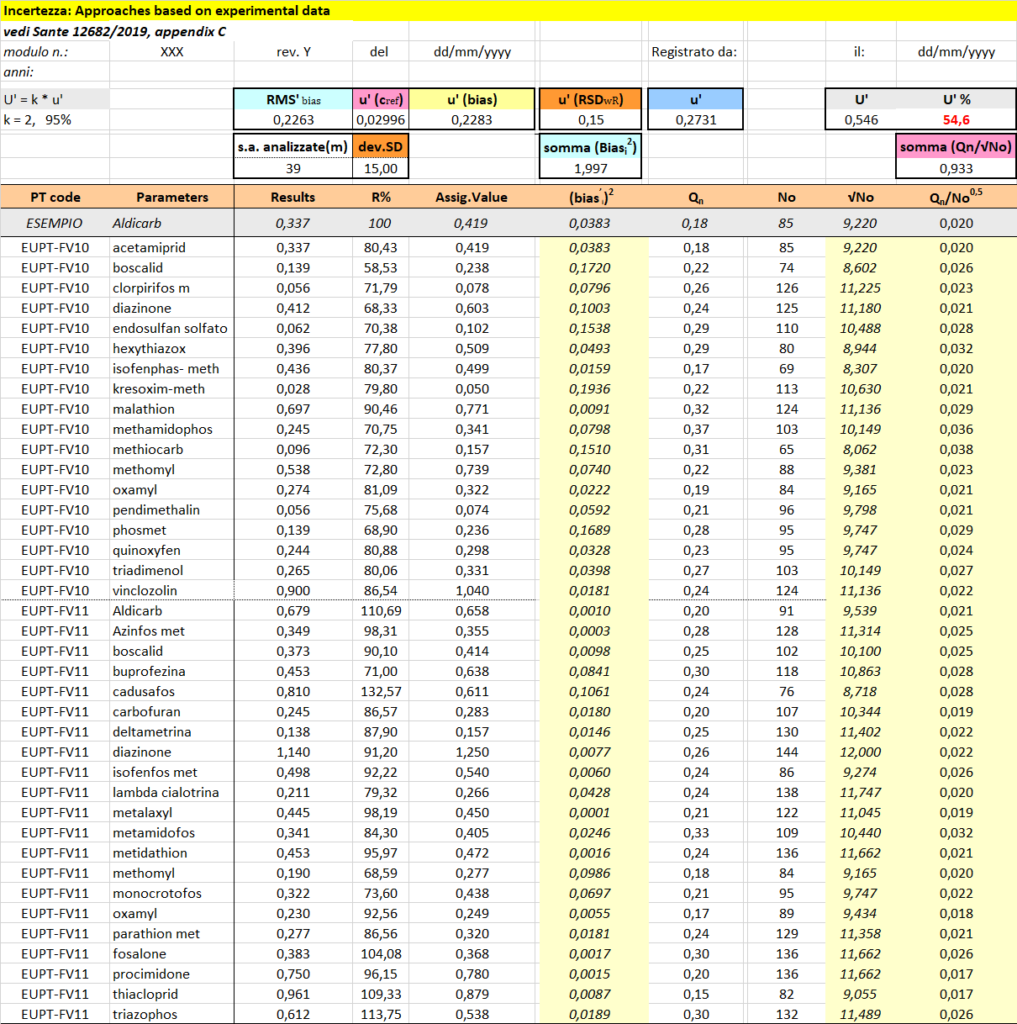
- PT code: codice del PT (prima colonna)
- Parameters: nome del parametro (seconda colonna)
- Results: risultato dell’analisi per il PT (terza colonna)
- R%: recupero percentuale del parametro (quarta colonna)
- valore assegnato o mediana “Assig.Value” (quinta colonna)
- la dispersione dei dati “Qn” espressa attraverso la deviazione standard robusta (settima colonna)
- il numero “No” dei laboratori che hanno inviato risultati per la specifica sostanza chimica (ottava colonna)
Invece i dati riportati nelle colonne di colore giallo sono dei calcoli:
- Biasi2 (sesta colonna) è un calcolo: ((results – Assig.value)/Assig.Value))2;
- √No: rappresenta la radice quadrata di m (nona colonna);
- Qn/√No: è il rapporto fra Qn e la radice quadrata di No (ultima colonna).
Esame dei calcoli
La deviazione standard (dev.SD) dei valori di recupero espressa con lo scarto tipo è 15 % a cui corrisponde un contributo di incertezza 0.15 (u’Rw).
La relazione matematica 11 descritta precedentemente può essere scritta:
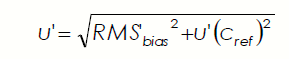
dove:
- RMSbias: è la radice quadrata della media della somma dei bias (campo (biasi)^2) divisa per il numero di sostanze attive analizzate (campo s.a. analizzate (m))
- u'(Cref): è calcolato facendo la somma del Qn diviso per la radice quadrata del numero di risultati riportati dai laboratori per ciascuno dei pesticidi, poi diviso per il numero m di pesticidi e moltiplicato per un fattore 1.253 in accordo con la ISO 13528.
u’Bias
Si calcolano dalle seguenti relazioni:
RMSBias = (somma (Biasi2)/m)0.5 = (1.9973/39)0.5 = 0.2263
u'(Cref) = (somma (Qn/√No)/m) * 1.253 = 0.9326/39 * 1.253 = 0.02996
Combinando RMSBias e u'(Cref) si calcola u’Bias:
u’Bias = (0.22632+0.029962)0.5 = 0.2283
u’ (RSDwR)
Nella tabella 1 e nel documento Sante 12682/2019 lo scarto tipo ottenuto dai dati del recupero è 15 e quindi
u´(RSDwR) = 0.15
Incertezza composta
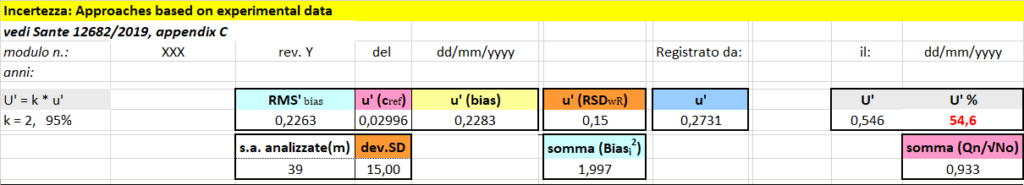
Combinando u’Bias con u’ (RSDwR) si calcola u’:
u’ = (0.22832+0.152)0.5 = 0.2731
come si può vedere dalla tabella 2 seguente.
Incertezza estesa
Immediato è il calcolo dell’incertezza estesa dalla relazione matematica:
U’ = K * u’ = 2 * 0.2731 = 0.546
che equivale al:
54.6 % (campo U’%).
Nota:
I colori identici (tabella 2) nei diversi campi servono per indicare quali parametri sono coinvolti nelle formule matematiche che determinano i valori di: RMSBias, u'(Cref) e u'(RSDwR).
La leggera differenza di somma (Biasi2) ed u’ è dovuta ai valori decimali.
Si suggerisce di monitorare nel tempo l’incertezza calcolata con questa modalità per valutarne la tendenza.
Norme
Sante/12682/2019 Analytical quality control and method validation procedures for pesticide residues analysis in food and feed
Per saperne di più
EURL, https://www.eurl-pesticides.eu
Bibliografia
[1] Sante/12682/2019 Analytical quality control and method validation procedures for pesticide residues analysis in food and feed
[2] UNI EN 15662:2018 Alimenti di origine vegetale – Multimetodo per la determinazione dei residui di pesticidi utilizzando GC e LC dopo estrazione/separazione con acetonitrile e purificazione mediante SPE dispersiva – Metodo modulare QuEChERS
Autore Marco Morelli
Aggiornamento del 06/11/2020